Cart (0 Items)
Your cart is currently empty.
View ProductsYou're visiting from outside the EU. Switch to the US version to see local pricing and tax details in USD.
Switch to US ($)
ProteoGenix s’adapte à chaque projet pour atteindre vos objectifs dans les plus brefs délais :
Contourner les problèmes d’immunogénicité
Pour une cible donnée
Délai d’obtention court
Exemple : 3-4 mois pour un criblage à partir d’une bibliothèque naïve contre 9 mois pour la technologie hybridome classique afin d’obtenir un anticorps recombiné purifié !
Protection animale
Très grande diversité de variants testés
Nous travaillons sur d’importantes bibliothèques allant jusqu’à 1010 variants, issues de dizaines de donneurs et d’un mélange de différentes souches/groupes ethniques pour maximiser le répertoire d’anticorps.
Pas besoin de rehumanisation ultérieure
Économisez du temps, des efforts et de l’argent grâce à nos bibliothèques naïves humaines et accélérez grandement votre accès à la clinique !
| Bibliothèque | Format | Espèce | Taille (clones) | Type de bibliothèque |
|---|---|---|---|---|
| LiAb-SFCOVID-19TM | scFv | Humain – Donneurs ayant récupéré de la COVID-19 – Idéal pour génération d’anticorps anti-COVID-19 | 1,19 × 1010 | Immunisée |
| LiAb-SFCANCERTM Library | scFv & Fab | PBMC & BMMC issu de donneurs humains (86 patients atteints de 18 cancers différents) :
|
|
Immunisée |
| LiAb-SFAUTOIMMTM Library | scFv & Fab | PBMC & BMMC issus de donneurs humains (57 patients avec 12 maladies auto-immunes différentes) :
|
|
Immunisée |
| LiAb-SFMAXTM | scFv & Fab | Humain – 5 groupes ethniques différents – 368 donneurs | 5,37 × 1010 | Naïve |
| LiAb-SFaTM | scFv | Humain | 1,5 × 109 | Naïve |
| LiAb-FabTM | Fab | Humain | 2,00 × 1010 | Naïve |
| LiAb-SFDogTM | scFv & Fab | 46 chiens sains de 6 races différentes : Beagle, Berger allemand, Labrador, English Coonhound, Dogue allemand, Chien rural chinois |
|
Naïve |
| LiAb-SFCatTM | scFv & Fab | 52 chats sains de 8 races différentes (Ragdoll, Maine Coon, Persan, Européen à poils courts, Européen à poils longs, American Shorthair, Siamois, Bengal) |
|
Naïve |
| NOUVEAU ! LiAb-VHHMAXTM |
VHH | Chameau, lama, alpaga – 57 animaux – Idéal pour la génération de protéines NANOBODY®* | 1,51 × 1010 | Naïve |
| LiAb-SFRabTM | scFv & Fab | Lapin – 4 races différentes pour une diversité maximale | 1,09 × 1010 | Naïve |
| LiPep-12 | Peptide 12-mer | / | 1,00 × 109 | Naïve |
| LiPep-7 | Peptide 7-mer | / | 1,00 × 109 | Naïve |
Nous proposons plus de bibliothèques au format scFv car elles présentent une stabilité génétique supérieure à celle du format Fab.
Cependant, le format Fab permet une sélection simplifiée des réactifs (en évitant la formation de dimères ou trimères).
D’autres bibliothèques d’autres espèces peuvent être disponibles sur demande.
Un criblage de la bibliothèque sélectionnée est réalisé par ELISA afin d’identifier les liaisons à haute affinité à la protéine d’intérêt. Pendant l’interaction entre les binders et la protéine, les binders restent fixés au puits, tandis que les non-binders sont éliminés par lavage.
Les binders sont élués puis récupérés pour infecter des bactéries (avec un helper phage) et augmenter leur quantité. La répétition de cette méthode, appelée « panning » (ou « biopanning »), permet de sélectionner les meilleurs binders, qui sont ensuite isolés pour validation en ELISA.
Enfin, l’ADN des meilleurs binders est séquencé, permettant leur production en tant que protéines recombinantes. ProteoGenix réalise en général 3 à 5 étapes de panning afin de vous garantir les meilleurs candidats possibles.
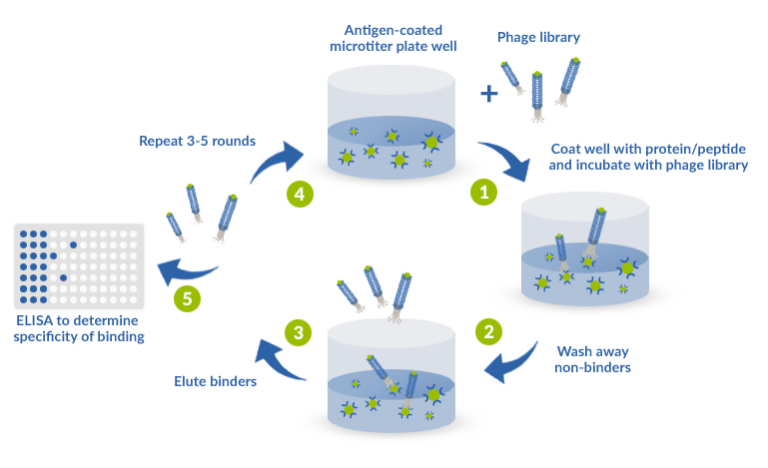
Toutes les séquences peuvent être fournies au client. ProteoGenix garantit 3 à 10 binders, mais il est possible d’en obtenir davantage sur demande. Une maturation d’affinité peut ensuite être réalisée avec les meilleurs binders si nécessaire.
Pour plus d’informations ou pour obtenir un devis concernant nos services de phage display avec utilisation de bibliothèques naïves, contactez-nous.
Sections associées susceptibles de vous intéresser :
*NANOBODY® est une marque déposée de Ablynx N.V.
